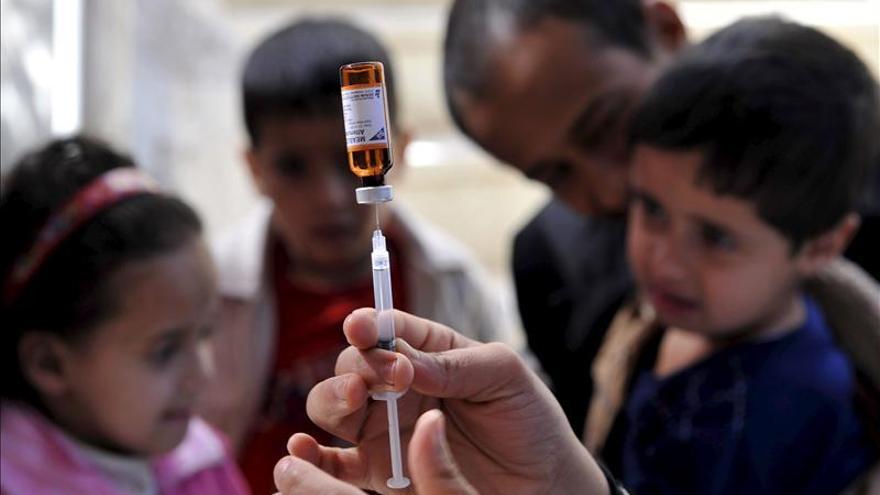
Inmunizar a los niños o no es una cuestión de dinero. O al menos es el caso de la vacuna contra el neumococo, que no fue incluida en el primer calendario común de vacunación, creado en 2013. Hace dos años se argumentó que no se podía afrontar su financiación pública. Así,
España quedaba como único bastión en Europa occidental, junto a Portugal, en el que no se realizaba una vacunación sistemática y generalizada contra esta bacteria, según reflejaba un informe de situación del Centro de Control de Enfermedades.
Por entonces Sanidad rebajaba la importancia de la protección generalizada contra un virus que puede causar neumonías y meningitis. Madrid la aplicaban a los bebés, pero también con criterios presupuestarios dejó de hacerlo en 2012, una decisión refrendada por el criterio de Sanidad, que no la incluyó en el catálogo obligatorio de vacunas. Pero lo que antes no hacía falta ahora es de interés general. Y el Prevenar13 empezará a dispensarse en todo el país en 2016.
Lo decidió hace unas semanas el Consejo Interterritorial de Salud, en medio de la vorágine sobre los tratamientos de la hepatitis C. La financiación pública de esta vacuna no es una porción de presupuesto desdeñable para las comunidades autónomas: la Comunidad de Madrid adquirió en 2009
634.350 dosis por 28,8 milllones de euros.
La exclusión de la vacuna del neumococo fue muy criticada, por ejemplo,
por los pediatras. La Asociación Española de Pediatría consideraba que "la ausencia de esta vacunación antineumocócica en el calendario común es especialmente lesiva para la prevención infantil española". El propio Ministerio de Sanidad admitió en noviembre que se había dado un "leve" repunte de la infección por neumococo.
Tres veces más letal que la gripe
Hasta la eliminación de este suero del calendario de mínimos, las experiencias se habían centrado en Madrid y Galicia. La primera eliminó la vacunación en su primer batería de recortes en 2012 y quedó restringida a grupos de riesgo, como recogía
la instrucción de la Dirección General de Atención Primaria: la adquisición de dosis para 2014 fue de
60.000 unidades y 2,5 millones de euros. En Galicia se paró alegando que se trataba de un "
proyecto piloto" ya terminado.
Pero aunque las autonomías no la pagaban, el Ministerio de Sanidad sí permitía que la vacuna se aplicara de manera particular, es decir, pagada por las familias. Cada dosis costaba en el mercado unos 78 euros –hay que aplicar cuatro–. A las administraciones el laboratorio dueño de la patente, Pfizer, se las deja a 45 euros.
Así, en abril del año pasado, durante la Semana Mundial de la Vacunación, en unas jornadas organizadas por el laboratorio Pfizer, se hacía hincapié en la singularidad española respecto a este producto. La Sociedad Española de Médicos de Atención Primaria (SEMERGEN) subrayaba su malestar por haberse eliminado el Prevenar 13 de la financiación pública (y por tanto de la administración generalizada).
Allí compartieron espacio la coordinadora del Grupo de Trabajo de de Actividades Preventivas de la SEMERGEN, Esther Redondo, con la responsable médico de vacunas de Pfizer, Cristina Méndez.
La doctora Redondo –que es miembro del Comité Asesor de Vacunas de la Comunidad de Madrid– aseguraba en octubre, durante la presentación de la campaña de vacunacion de la gripe, que la prevención del neumococo era "tan importante" como la de la gripe al tiempo que recordaba que su letalidad triplica a la de esta última.
La más vendida
La Organización Mundial de la Salud (OMS) recomendó en 2012 la vacunación extensa contra la Streptococcus pneumoniae. La administración de este suero es, por tanto, un nicho de ventas masivo para las farmacéuticas: basta con comprobar cómo la cuantía de los contratos firmados por la Comunidad de Madrid se dividieron por 10 entre 2009 y 2014.
La vacuna 13 valente para esta infección es la más vendida del mundo. Prevenar 13, el producto del laboratorio Pfizer, vendió unos 2.000 millones de euros en 2010, según una revisión de la OMS. En 2012 ya estaba en 3.290 millones de euros y en 2013 en más de 3.300. Se situó en el puesto 21 de todos los productos farmacéuticos. La otra composición recomendada por la OMS, la decavalente fabricada por GlaxoSmithKline, llamada Synflorix, vendía seis veces menos en 2012.
La patente de Prevenar 13 es pues un tesoro para Pfizer. La dueña primigenia de este suero era otro laboratorio llamado Wyeth Lederle. De hecho su filial Wyeth Farma era la adjudicataria de las adquisiciones públicas en España. En enero de 2009, Pfizer (la mayor fabricante de medicamentos del mundo)
admitió que había pagado 5.800 millones de euros por hacerse con esta rival. Con la absorción se quedó con Prevenar 13.






![[Img #24548]](http://noticiasdelaciencia.com/upload/img/periodico/img_24548.jpg)




